# 用Otsu阈值与形态学方法实现分割医学CT中的肺部
# 目录
# 简介
本教程介绍如何用Otsu阈值与形态学方法实现分割医学CT中的肺部。本方法无需深度学习,完全基于传统图像处理算法,可自动获得三维肺部掩码,适合医学影像处理初学者和进阶用户。
源码可在GitHub获取。
# 环境准备
请确保安装如下Python库:
pip install numpy opencv-python nibabel matplotlib scipy# 方法原理
本方法主要包含以下步骤:
- 窗宽窗位调整:将CT值归一化到合适的灰度范围(肺窗)
- Otsu阈值分割:自动分割肺部与其他组织
- 去除背景和小连通域:只保留肺部结构
- 洞填充与形态学闭操作:修复掩码边缘
- 三维连通域分析:自适应保留最大两个肺部区域
# 完整代码与流程讲解
# 4.1 CT窗函数调整
def ct_window(img, WL=-600, WW=1500):
img = np.clip(img, WL - WW // 2, WL + WW // 2)
img = (img - (WL - WW // 2)) / WW * 255.0
return img.astype(np.uint8)作用:将CT原始值(HU值)通过窗宽窗位调整到适合显示和处理的灰度范围。肺窗常用参数:WL=-600, WW=1500。
# 4.2 逐层Otsu二值化
def otsu_3d(img_3d):
binary_3d = np.zeros_like(img_3d, dtype=np.uint8)
for i in range(img_3d.shape[2]):
_, binary_3d[:, :, i] = cv2.threshold(img_3d[:, :, i], 0, 255, cv2.THRESH_BINARY + cv2.THRESH_OTSU)
return binary_3d作用:对每一层切片使用Otsu算法自动阈值分割,得到初步的二值掩码。
# 4.3 去除与背景连通的区域
def remove_background_2d(binary_3d):
out = np.zeros_like(binary_3d, dtype=np.uint8)
for i in range(binary_3d.shape[2]):
binary_slice = binary_3d[:, :, i]
ex = cv2.copyMakeBorder(binary_slice, 3, 3, 3, 3, cv2.BORDER_CONSTANT, value=0)
cv2.floodFill(ex, None, (0, 0), 255)
mask = ex == 0
result = np.zeros_like(binary_slice)
result[mask[3:-3, 3:-3]] = 255
out[:, :, i] = result
return out作用:去除与图像边缘(背景)连通的区域,只保留肺部等内部结构。
# 4.4 去除小连通域
def remove_small_objects(mask, min_area=1000):
num_labels, labels, stats, _ = cv2.connectedComponentsWithStats(mask, connectivity=8)
out = np.zeros_like(mask)
for i in range(1, num_labels): # 0是背景
area = stats[i, cv2.CC_STAT_AREA]
if area >= min_area:
out[labels == i] = 255
return out作用:去除面积较小的连通区域(如噪声),只保留较大的结构(肺部)。
# 4.5 洞填充
from scipy.ndimage import binary_fill_holes
def fill_holes_3d(mask_3d):
filled = np.zeros_like(mask_3d)
for i in range(mask_3d.shape[2]):
filled[:, :, i] = binary_fill_holes(mask_3d[:, :, i] > 0).astype(np.uint8) * 255
return filled作用:填补掩码内部的空洞,确保肺部区域完整。
# 4.6 闭操作修复边缘
def morph_close_3d(mask_3d, kernel_size=5):
kernel = cv2.getStructuringElement(cv2.MORPH_ELLIPSE, (kernel_size, kernel_size))
closed = np.zeros_like(mask_3d)
for i in range(mask_3d.shape[2]):
closed[:, :, i] = cv2.morphologyEx(mask_3d[:, :, i], cv2.MORPH_CLOSE, kernel)
return closed作用:平滑边缘,去除小孔和断裂。
# 4.7 3D连通域分析
from scipy.ndimage import label
def keep_largest_objects_adaptive(mask_3d, area_ratio_thresh=5.0):
labeled, num = label(mask_3d > 0)
if num <= 2:
return (mask_3d > 0).astype(np.uint8) * 255
counts = np.bincount(labeled.flat)
areas = counts[1:] # counts[0]是背景
if len(areas) < 2:
mask = (labeled > 0)
return (mask * 255).astype(np.uint8)
sorted_idx = np.argsort(areas)[::-1]
area1, area2 = areas[sorted_idx[0]], areas[sorted_idx[1]]
label1, label2 = sorted_idx[0]+1, sorted_idx[1]+1
if area1 > area_ratio_thresh * area2:
mask = (labeled == label1)
else:
mask = np.isin(labeled, [label1, label2])
return (mask * 255).astype(np.uint8)作用:在三维上只保留最大的1-2个连通区域(通常为左右肺),自适应处理连在一起的情况。
# 4.8 主流程与可视化
import nibabel as nib
import numpy as np
import cv2
import matplotlib.pyplot as plt
def lung_mask_pipeline(nii_path, out_path):
# 读取CT
nii = nib.load(nii_path)
img_3d = nii.get_fdata()
img_3d = ct_window(img_3d)
# 逐步处理
binary_3d = otsu_3d(img_3d)
binary_3d_no_bg = remove_background_2d(binary_3d)
min_area = 1000
clean_3d = np.zeros_like(binary_3d_no_bg, dtype=np.uint8)
for i in range(binary_3d_no_bg.shape[2]):
clean_3d[:, :, i] = remove_small_objects(binary_3d_no_bg[:, :, i], min_area=min_area)
filled_3d = fill_holes_3d(clean_3d)
closed_3d = morph_close_3d(filled_3d, kernel_size=5)
lung_mask_3d = keep_largest_objects_adaptive(closed_3d)
# 保存NIfTI掩码
final_nii = nib.Nifti1Image(lung_mask_3d, affine=nii.affine, header=nii.header)
nib.save(final_nii, out_path)
print(f'最终3D二值化肺掩码已保存为 {out_path}')
# 可视化
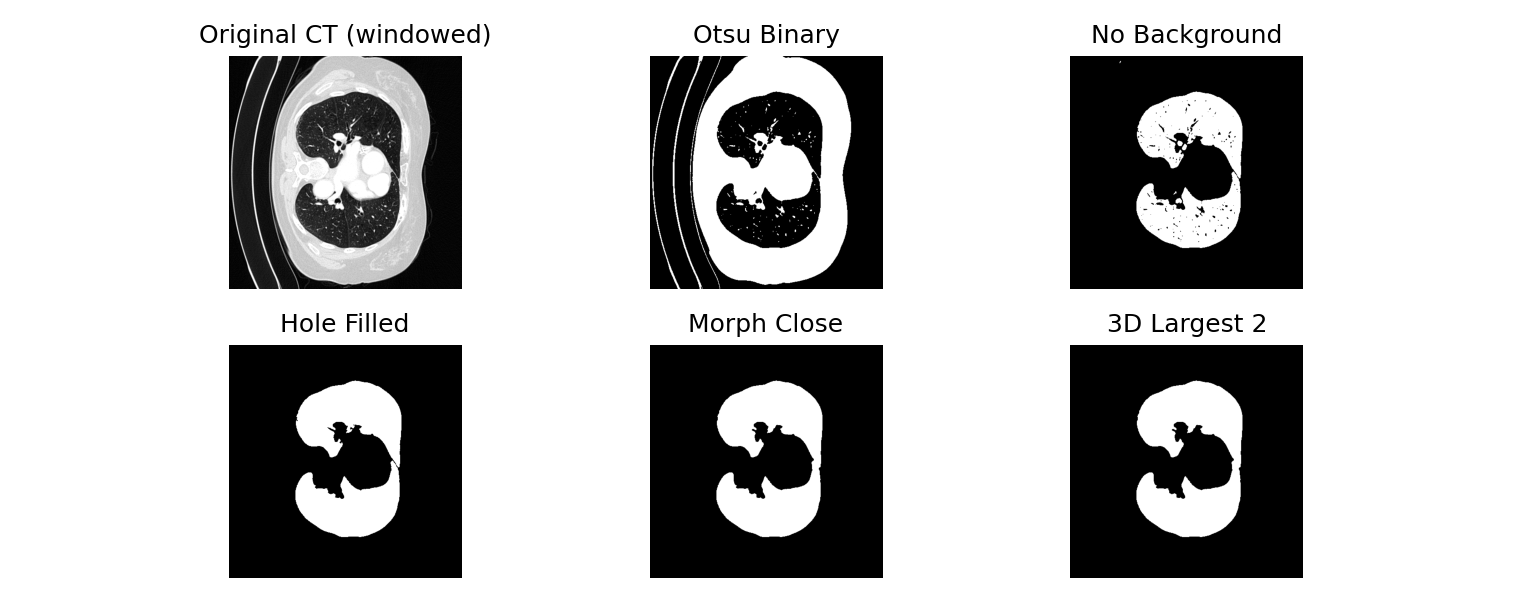
slice_id = img_3d.shape[2] // 2
plt.figure(figsize=(24, 4))
plt.subplot(1, 6, 1)
plt.title('Original CT (windowed)')
plt.imshow(img_3d[:, :, slice_id], cmap='gray')
plt.axis('off')
plt.subplot(1, 6, 2)
plt.title('Otsu Binary')
plt.imshow(binary_3d[:, :, slice_id], cmap='gray')
plt.axis('off')
plt.subplot(1, 6, 3)
plt.title('No Background')
plt.imshow(binary_3d_no_bg[:, :, slice_id], cmap='gray')
plt.axis('off')
plt.subplot(1, 6, 4)
plt.title('Hole Filled')
plt.imshow(filled_3d[:, :, slice_id], cmap='gray')
plt.axis('off')
plt.subplot(1, 6, 5)
plt.title('Morph Close')
plt.imshow(closed_3d[:, :, slice_id], cmap='gray')
plt.axis('off')
plt.subplot(1, 6, 6)
plt.title('3D Largest 2')
plt.imshow(lung_mask_3d[:, :, slice_id], cmap='gray')
plt.axis('off')
plt.tight_layout()
plt.show()# 运行与结果
# 输入与输出
- 输入:三维CT影像(NIfTI格式,
.nii或.nii.gz) - 输出:三维肺掩码(NIfTI格式,
lung_mask_final.nii.gz)
# 运行示例
lung_mask_pipeline('your_ct.nii.gz', 'lung_mask_final.nii.gz')处理过程会自动显示每一步的中间结果,直观展示肺部分割效果。
# 总结
本教程完整演示了用Otsu阈值与形态学方法实现分割医学CT中的肺部的全流程。该方法无需训练模型,适合快速肺部ROI提取,也可作为深度学习分割的预处理。你可以根据实际需求调整参数(如min_area、kernel_size、窗宽窗位等)。
# 参考资料
如需分割其他医学结构,只需调整阈值与区域筛选条件即可。
如有问题欢迎随时提问!